Slt ! Je vais reprendre un peu tout ça car il y a des erreurs :
1)
Qu'est-ce qu'une séquence consensus ? 
C'est une séquence d'AA, courte qui va être reconnu par une enzyme
Ex des protéines kinases : Ce sont des protéines capables de phosphoryler des protéines au niveau de résidus S,T,Y. Ces kinases ne peuvent pas phosphoryler n'importe quel résidus S,T,Y... Il faut phosphoryler le ou les résidus qui vont permettre la régulation de la protéine phosphorylée (ex: les sérine 14 de la GP).
Comment on distingue LE résidu à phosphoryler des autres?

la kinase reconnait non pas le résidu S,T,Y seul mais les résidus S,T,Y placés dans une séquence d'AA particulière !
Ex : X-X-Tyr-X-X ou les X sont des AA bien définis. Par ex, la PKA phosphoryle des Sérines ou des Thréonine inclues dans une séquence de type Arg-Arg-X-
Sér/Thr (X est n'importe quel AA).
On appelle ces séquences, les
séquences consensus : elles sont reconnues par le sites de fixation de l'enzyme et le site catalytique va agir uniquement sur la Sérine/Thréonine/Tyrosine présente dans la séquence consensus !
2)
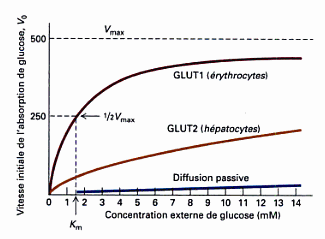
Capacité / Affinité, c'est quoi ?Le transport facilité du glucose grace aux GLUT est similaire à une réaction enzymatique :
GLUT + Glucose (extracellulaire) <=> complexe GLUT/Glucose <=> GLUT + Glucose (intracellulaire)Cette réaction possède :
- un
Km =
affinité de GLUT pour le Glucose- une
Vm =
capacité de transfert du Glucose par GLUT  Ces deux grandeurs sont indépendantes les unes des autres
Ces deux grandeurs sont indépendantes les unes des autres.
Dawn, la notion d'affinité et de capacité ne sont pas liées car certes plus le Km est faible plus le glucose est heureux d'être avec son GLUT, mais si ce GLUT a une Vm élevée, il va quand même très vite faire passer du glucose à l'intérieur de la cellule !Ex de GLUT4 : Faible Capacité (faible Vm) mais Forte Affinité (faible Km)
Pour atteindre une vitesse x de transport de glucose dans les muscles/coeur/TA, il faut peu de glucose ! C'est totalement adapté pour capter le glucose dans le sang lors de l'hyperglycémie post prandiale (qui n'est jamais très importante)
La Vm sera atteinte pour des concentration en glucose pas si importante ! GLUT4 est facilement saturable
Ex de GLUT 2 : Faible Affinité (fort Km) mais Forte Capacité (faible )
Pour atteindre la même vitesse x de transport de glucose dans le foie ou les cellules béta, il faut bcp de glucose ! C'est adapté pour capter la très grande quantité de glucose qui arrive au foie par la veine porte
La Vm sera atteinte pour des concentrations très haute, GLUT 2 est difficilement saturable !
La formule est la suivante :
Vr = (Vm x S) / (Km + S)Je vous rappelle aussi que k1 et k-1 NE VARIENT PAS !! Ce sont des CONSTANTES de vitesse ^^
Regardez ce graphe, on l'on compare la cinétique de GLUT2 et GLUT1 (GLUT1 a une cinétique similaire à GLUT4):
- Capture d’écran 2012-10-26 à 21.53.56.png (34.52 Kio) Vu 1573 fois
ça va mieux ?






 Juste une petite synthese :
Juste une petite synthese :



